… und muss womöglich aus den Lehrbüchern gestrichen werden. Diesmal im Visier: die 30-nm-Chromatinfaser.
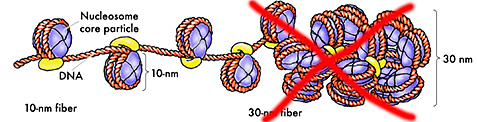
Im „Kompaktlexikon der Biologie“ auf wissenschaft-online.de steht etwa noch zur Chromatinstruktur (wie an vielen anderen Stellen auch):
Grundbausteine des Chromatins sind feine fädige, etwa 10 nm dicke Stränge, die Nucleofilamente oder Chromonemen, die aus einer Folge von Nucleosomen aufgebaut sind (Nucleosom). Die Nucleofilamente sind ihrerseits zu einer Überstruktur, der 30-nm-Chromatinfibrille, aufgeknäuelt, die schraubenförmig als Solenoid aufgewunden ist, sodass eine röhrenförmige Struktur entsteht.
Kanadische Forscher schauten jetzt mit neuester 3D-bildgebender Technik tief in intakte Mäusezellen hinein und fanden in den Zellkernen — … nirgendwo irgendwelche 30-nm-Fasern (EMBO reports advance online publication; doi:10.1038/embor.2012.139)
Im Abstract schreiben sie:
Here, by combining electron spectroscopic imaging with tomography, three-dimensional images are generated, revealing that both open and closed chromatin domains in mouse somatic cells comprise 10-nm fibres. These findings indicate that the 30-nm chromatin model does not reflect the true regulatory structure in vivo.
Seniorautor David Bazett-Jones von der Universität Toronto erklärt dazu in einer Pressemeldung:
Our results revealed that the 30-nm chromatin fibre model is not consistent with the structure we found in our three-dimensional spectroscopic images. It was previously thought that the transition between thinner and thicker fibres represented a change from an active to repressed state of chromatin. However, our inability to detect 30-nm fibres in the mouse genome leads us to conclude that the transcriptional machinery has widespread access to the DNA packaged into chromatin fibres.
Warum wurden zuvor aber derart viele 30-nm-Fasern beobachtet und fotografiert? Zum Beispiel diese:
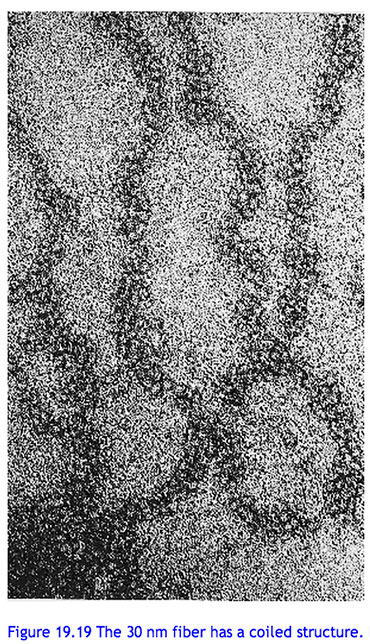
Dazu heißt es in der Pressemeldung:
The researchers offer several reasons for the observation of wider fibres in earlier studies. In some cases, the conditions outside of the cell, including those used in earlier studies where chromatin was extracted from the cell, may have given rise to structural artifacts. For some of the earlier spectroscopic studies, it may even be a question of poor resolution of existing 10-nm fibres.
Am ehesten also Präparations-Artefakt, hin und wieder eventuell auch zu schwache Auflösung.
In diesem Zusammenhang können wir uns eine Randnotiz nicht verkneifen: Nähme man die beiden PLOS-Editorinnen Virginia Barbour und Kasturi Haldar ernst, die gerade frisch gefordert haben, jede Studie komplett zurückzuziehen, deren grundlegende Schlussfolgerung sich als falsch herausstellt (siehe Laborjournal online) — man hätte jetzt ordentlich zu tun.
Schlagworte: Artefakt, Chromatin, Fibrillen, Lehrbuch, Retraktion, Spektroskopie, Zellen






Na, eigentlich schon fast ein alter Hut ! (Eltsov M, Maclellan KM, Maeshima K, Frangakis AS, Dubochet J 2008, Analysis of cryo-electron microscopy images does not support the existence of 30-nm chromatin fibers in mitotic chromosomes in situ. Proc Natl Acad Sci USA 105: 19732–19737). Aber Presseleute brauchen eben Presserummel, um etwas mitzukriegen …
Stimmt, die Sache schwelt schon länger — siehe auch hier. Danke für den Hinweis. Allerdings „Presserummel“? Wir haben’s in der Presse nirgendwo gefunden, es gibt nur die Pressemeldung von EMBO Reports…
‚tschuldigung, blanke Polemik. Pressemeldung zur eigentlichen Veröffentlichung ist für mich halt schon „Presserummel“, aber ich bin auch medieninkompetent (und lasse mein Handy meist ausgeschaltet). Und ihr da bei LJ seid auch keine „Presseleute“, sondern Wissenschaftler, die sich nützlich machen; für mich auch ohne den etwas bärbeißig gewordenen Hubert R. weiterhin erste Adresse für differenzierte/unabhängige und sogar oft unterhaltsame Berichterstattung aus den (teutschen) Lebenswissenschaften (nebst angeschlossener Politiklandschaft).
Apropos: Vielleicht bietet die o.g. story mehr („how to fight a dogma“), redet doch mal mit Eltsov & Co. (Frankfurt, Frangakis) – die ärgern sich jetzt vielleicht, daß sie 2008 nicht gleich genereller gesagt haben „no 30 nm“, nicht nur in Chromosomen (vielleicht mußten sie ihr kompliziertes polymer-melt „erfinden“, um bei PNAS durchzukommen). In Frankfurt/M. ließe sich gleich ein ganzes cryo-EM special machen, da gibt’s auch den Herrn Kühlbrandt …