Die Wächter des Poren-Tores
(18.12.17) Hin und wieder kann man eine Pressemitteilung über Forschungsergebnisse ruhig auch mal auf andere Art formulieren. Etwa so, wie das Max-Planck-Institut für Biochemie gerade Neues über die "Superhelden" des Kernporen-Transports mitgeteilt hat.
in Tor zwischen zwei Welten hat sich geöffnet. Eindringlinge des einen Universums stürmen das Tor. Gelangen sie hindurch, wird das zweite Universum ins Chaos gestürzt. Gerade wenn alle Hoffnung verloren scheint, kommen Wächter herbei und bekämpfen die Eindringlinge. Es mag wie eine Szene aus einem Science-Fiction-Film oder einem Comic-Buch klingen, aber es findet tatsächlich in der Zelle, an der Schnittstelle zwischen Zytoplasma und dem Zellkern statt.
Zelluläre Superhelden
Wusstet ihr, dass es Superhelden in der Zelle gibt? Diese Helden werden Proteasomen genannt. Sie sind große Proteinkomplexe, die die Zelle verteidigen, indem sie fehlgefaltete Proteine zerstören. Ohne Proteasomen sind Zellen schutzlos und können gefährliche Proteine nicht beseitigen. Letztendlich sterben die Zellen. Die Bedeutung der Proteasomen für Zellen ist schon lange bekannt. Aber wie stellt eine Zelle sicher, dass genügend Proteasomen zur richtigen Zeit am richtigen Ort sind? Um dieser Frage nachzugehen, nutzten Forscher der Abteilung „Molekulare Strukturbiologie„ die Kryo-Elektronentomographie (Kryo-ET) um Proteasomen in ihrer natürlichen Zellumgebung darzustellen.
Freeze! Schnappschüsse von Proteinen in Aktion
Bei der Kryo-ET werden Zellen rasch eingefroren und mit einem fokussierten Ionenstrahl ausgedünnt, um transparente „Fenster“ in die Zelle zu schneiden. An einem Transmissionselektronenmikroskop werden Abbildungen der „Fenster“ erstellt. Die resultierenden dreidimensionalen Bilder, Tomogramme genannt, zeigen das Zellinnere in ihrem ursprünglichen Zustand und mit einer Auflösung, die hoch genug ist, um die feinen Details der Proteinstrukturen zu erkennen. „Es ist eine revolutionäre Technik“ , erklärt Sahradha Albert, Erstautor der Studie. „Wir tauchen in eine ganz neue Welt ein – eine Welt, die bis jetzt für uns unsichtbar war. Diese Studie enthält die meisten zellulären Tomogramme, die je für ein Projekt kombiniert wurden. Die Abbildung von so vielen Proteasomen ermöglichte uns, die funktionellen Zustände und Bindungswechselwirkungen jedes Proteasoms zu untersuchen.“
Eine neue Funktion der Proteasomen: Kernporenkomplex-Kontrolle
Zu ihrer Überraschung entdeckten Albert und Kollegen, dass viele Proteasomen an Kernporenkomplexe gebunden waren, die als Gateway für den Transport von Molekülen zwischen Zytoplasma und Zellkern dienen. Spezielle Proteine heften die Proteasomen an zwei Stellen auf der Kernseite des Komplexes an: an den Kernkorb des Komplexes und an die Membran, die den Kernporenkomplex umgibt. Die Forscher konnten auch zeigen, dass diese Proteasomen funktionell sind – sie wurden beim Abbau von Proteinen abgelichtet.
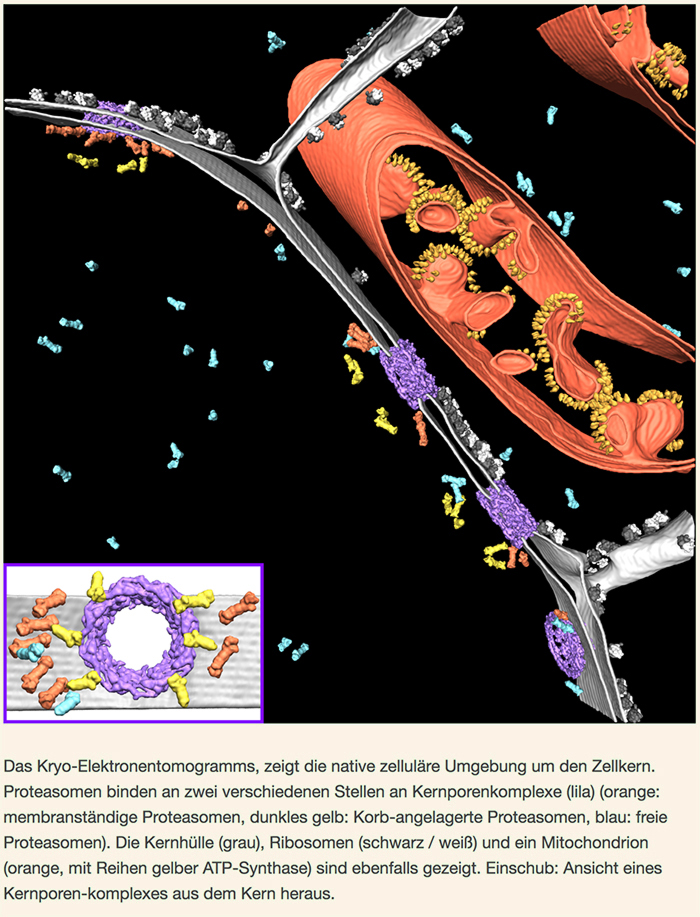
Damit größere Proteine den Kernporenkomplex passieren können, müssen sie von einem Protein namens Importin geleitet werden. Aber reicht das aus, um sicherzustellen, dass nur die richtigen Proteine durch das Tor kommen? Membranproteine und kleine lösliche Proteine passieren den Kernporenkomplex ohne Importin. Was passiert, wenn unerwünschte Proteine durch das Tor gelangen? Die Komplex-gebundenen Proteasomen könnten eine Antwort liefern. Durch Umkreisen der Kernporenkomplexe könnten diese Proteasomen Teil eines „Grenzkontroll“-Überwachungsmechanismus sein, bei dem unerwünschte Proteine, die durch den Komplex kommen, identifiziert und zerstört werden. „Diese bemerkenswerte Beobachtung bietet eine völlig neue Perspektive auf die Regulierung des Kernporenkomplex-Transports“, sagt Benjamin Engel, der korrespondierende Autor der Publikation. „Dennoch werfen unsere Ergebnisse viele Fragen auf. Unsere Studie ist wirklich nur die Spitze des Eisbergs.“
Das Superhelden-Team
Proteasomen verteidigen die Zelle nicht alleine. Wie die meisten Superhelden benötigen sie ein Unterstützer-Team. Während Proteasomen leistungsfähige Abbaumaschinen sind, benötigen sie die Hilfe anderer Proteine, um ihnen zu sagen, wohin sie gehen und was sie zerstören sollen. Die von Albert und Kollegen erzeugten hochauflösenden Strukturen zeigten, dass Anker an die Kernporenkomplex-lokalisierten Proteasomen gebunden sind. Es bleibt jedoch ein Rätsel, welche Proteine diese Ankerpunkte bilden und wie sie Proteasomen zum Komplex lotsen. Proteasomen bauen Proteine ab, die mit Poly-Ubiquitin-Ketten markiert wurden – Modifikationen, die von einer Klasse von Enzymen, die E3-Ligasen genannt werden, hinzugefügt werden.
Die Zelle hat Hunderte von verschiedenen Versionen dieses Enzyms und jedes erkennt verschiedene Zielproteine. Dies liefert eine Spezifität für den Proteinabbau, da die E3-Ligasen den Proteasomen selektiv mitteilen, was sie zerstören sollen. Die Frage ist, welche E3-Ligasen am Kernporenkomplex wirken. „Wir wissen, dass die Proteasomen beim Komplex eine wichtige Aufgabe erfüllen, indem sie Proteine überwachen, die durch das Tor gelangen“, sagt Engel. „Der nächste Schritt ist jedoch, die Proteine zu identifizieren, die mit dem Proteasom am Komplex arbeiten. Welche Proteine sind Mitglieder des Teams und wie wirken sie zusammen? Sobald wir das lernen, werden wir verstehen, wie und warum die Proteasomen das Tor zum Kern bewachen.“
Originalpublikation:
Sahradha Albert, Miroslava Schaffer, Florian Beck, Shyamal Mosalagantib, Shoh Asano,Henry F. Thomas, Jürgen M. Plitzko, Martin Beck, Wolfgang Baumeister, und Benjamin D. Engel. Proteasomes tether to two distinct sites at the nuclear pore complex. PNAS, 11. Dezember 2017, doi: 10.1073/pnas.1716305114.









